Модуль программного обеспечения для секвенирования нового поколения SEQNEXTдля анализадля захватадля картографии
Добавить в папку «Избранное»
Добавить к сравнению
Характеристики
- Функция
- для анализа, для захвата, для картографии
- Применение
- для лабораторий, для секвенирования нового поколения
Описание
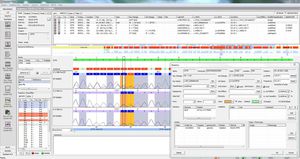
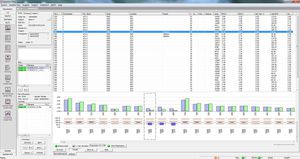
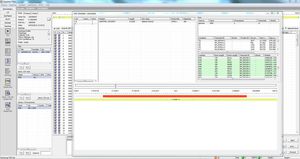
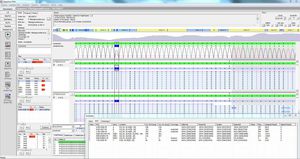
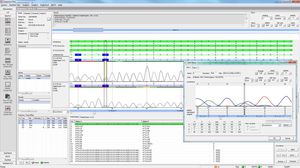
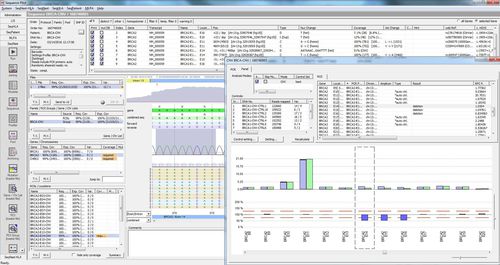
SEQNEXT - это мощное и удобное приложение для картирования, выравнивания и обнаружения вариантов в данных секвенирования следующего поколения. SEQNEXT может анализировать данные со всех распространенных платформ секвенирования и наборов (на основе ПЦР, обогащения, захвата последовательности). Визуализация всех обнаруженных вариантов, таких как делеции, инсерции и инделы любой длины, SNPs, повторяющиеся регионы, а также CNVs и слияния генов, понятна и интуитивно понятна.
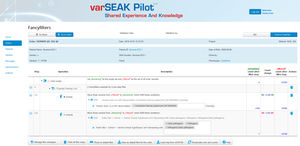
SEQNEXT предлагает доступ к публичным базам данных SNP, таким как dbSNP, 1000 Genomes, ClinVar, ExAC и gnomAD для классификации и фильтрации. Все данные результатов могут обмениваться с нашей базой данных вариантов для совместного опыта и знаний - varSEAK, передаваться во внутренние LIM-системы лаборатории и/или выдаваться в виде персонализированных отчетов для пациентов.
НОВОЕ Улучшенный анализ данных секвенирования вирусов, например, SARS-CoV-2
Триоанализ и улучшенный пул-анализ
Аннотации онтологии последовательностей в таблице вариантов
Возможность перехода к varSEAK и всем доступным внешним базам данных, таким как dbSNP, ClinVar, UK10K, ESP, gnomAD и ExAC
Анализ полноэкзомного секвенирования (WES)
Совместимость с данными всех распространенных платформ и наборов для секвенирования следующего поколения
Простая настройка отдельных целевых регионов (ROIs) посредством импорта bed- или manifest-файлов на основе hg19 и/или hg38
Импорт списков генов для фильтрации и анализа данных WES
Анализ fastq-, fastq.gz- или bam-файлов
Эффективные стандарты для картирования, выравнивания, качества и поиска вариантов (используемые алгоритмы: BWA и Smith-Waterman, адаптированные JSI)
Индивидуальные настройки для анализа и поиска вариантов (≥ 0,1 %)
Высокая чувствительность и специфичность для обнаружения делеций, вставок и инделов любой длины, SNPs, повторяющихся регионов, а также CNVs и слияний генов
---
Каталоги
SEQUENCE PILOT
2 Страницы
Другие изделия JSI medical systems
Products
* Цены указаны без учета налогов, без стоимости доставки, без учета таможенных пошлин и не включают в себя дополнительные расходы, связанные с установкой или вводом в эксплуатацию. Цены являются ориентировочными и могут меняться в зависимости от страны, цен на сырьевые товары и валютных курсов.